2 Transkriptom RNA Seq 1: Difference between revisions
| Line 67: | Line 67: | ||
== Assemblierung der reads == | == Assemblierung der reads == | ||
Aus der RNA-Seq erhaltene Fragmente sequenzierter RNA. Diese werden anschließend dem Referenzgenom (Template) zugeordnet werden. | |||
<big> | <big> | ||
Revision as of 21:20, 28 January 2021
Biologische Fragestellung
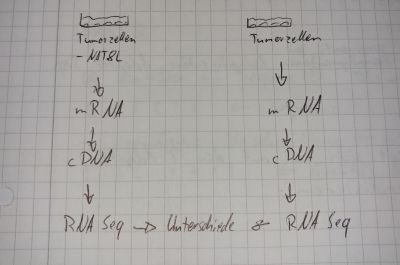
Da NAT8L in euren Prostatakarzinomzellen erhöht exprimiert ist, habt ihr euch entschlossen die Genexpression durch RNAi (RNA Interferenz) zu silencen.
Experiment
- Aus zwei Tumorzellkulturen wird die mRNA extrahiert
- mit Hilfe der reversen Transkriptase wird cDNA transkribiert
- cDNA wird sequenziert
- Sequenzunterschiede können analysiert werden
Sanger Methode
Als Wiederholung:
400px][https://de.wikipedia.org/wiki/DNA-Sequenzierung#Didesoxymethode_nach_Sanger
Next Generation Sequencing (NGS)
Illumina Sequencing (2nd Generation Sequencing)
Ergebnis der Illumina Sequenzierung:
- Länge der reads 50-600bp
- Fehlerrate ca. 0,1%
- humanes Genom kann 30x am Tag sequenziert werden
- Daten werden in FASTQ Format geliefert
FASTQ
Eine FASTQ-Datei ist folgendermaßen aufgebaut:
@ Identifier # Sequenz identifier GATCTT # Sequenz + # optionale Beschreibung !'CC'*+*!? # Qualität jedes Nukleotids (Zahlenwert repräsentiert durch ASCII Tabelle)
Problem
Viele kurze reads, die in einen Zusammenhang gebracht werden müssen!
Sequenzabdeckung
G: Länge der Genomsequenz
N: Anzahl der reads
L: durchschnittliche Länge der reads
C: Coverage (Abdeckung)
[math]\displaystyle{ C= \frac{N*L}{G} }[/math]
Lander-Waterman-Modell
Mathematisches Modell zur Errechnung, durch Sequenzierung, nicht abgedeckter Basenpaare.
P[nicht abgedecktes Bp] = e-c
Beispiele:
C=10 → 1 Gap in 22000 Bp
C=22 → 1 Gap in 3,6*109 Bp
C=30 → So tief, dass quasi alles überdeckt wird
Assemblierung der reads
Aus der RNA-Seq erhaltene Fragmente sequenzierter RNA. Diese werden anschließend dem Referenzgenom (Template) zugeordnet werden.
| -A | -C | -C | -T | -G | -A | -C | T | -A | -G | -C | -T | -G | -A | -T | -C | -A | -A | -G | -G | - | - | Template | |||
| -G | -A | -T | -C | -A | -A | ||||||||||||||||||||
| -A | -G | -C | -T | -G | -A | ||||||||||||||||||||
| -A | -C | G | -A | -G | -C | -T | - | - | Punktmutation | ||||||||||||||||
| -G | -A | -_ | -C | -A | -A | -G | -G | - | - | Deletion |