9 Biomarker: Difference between revisions
(Created page with "= Biomarker = '''Medizinische Biomarker'''<br> * Ein Biomarker ist ein messbarer Parameter biologischer Prozesse, der prognostische, oder diagnostische Aussagekraft hat und so...") |
No edit summary |
||
| Line 15: | Line 15: | ||
<math> logit_{(P)} = log \frac{P}{1-P} </math><br> | <math> logit_{(P)} = log \frac{P}{1-P} </math><br> | ||
* Damit wird die Wahrscheinlichkeit, dass jemand z.B. Krebs bekommt durch Gegenwahrscheinlichkeit bestimmt. | * Damit wird die Wahrscheinlichkeit, dass jemand z.B. Krebs bekommt durch Gegenwahrscheinlichkeit bestimmt. | ||
==Biomarkersignatur== | |||
Erweiterung für mehrere Gene. <br> | |||
<math> P(x) = \frac{1}{e^{-((\beta)_1 \cdot x_1) + ((\beta)_2 \cdot x_1) + .... + (\beta)_n \cdot x_n) + \beta_0)}}</math> <br> | |||
'''Mashine learning''' <br> | |||
* Ein Modell muss zunächst von einem System erlent werden, dann kann das System eine Aussage treffen, ob z.B. 'krank' oder 'gesund'. <br> | |||
* Parameter <math> \beta_1 </math> und <math> \beta_0 </math> können nicht berechnet werden. → Müssen mit Hilfe eines Algorithmus geschätzt werden. <br> <br> | |||
'''Maximum-Likelihood:''' <br> | |||
* Schätzung zur Parameterbestimmung. <br> | |||
* ''Training'': Lerndaten sind bekannte Werte zur Aussage 'krank' oder 'gesund' <br> | |||
→ Algorithmus bestimmt einen genauen Wert für <math> \beta_1</math>, um krank (1) und gesund (0) zu bestimmen. <br> | |||
→ Danach kann mit dem Modell bestimmt werden, ob es gut oder schlecht ist. <br> | |||
*'''Problem''': System versucht einen optimalen Wert zu finden <br> | |||
→ ''Overfitting'': Zu genaue Beschreibung des Modells.<br><br> | |||
'''Frage:''' Wie gut ist die Qualität des Modells? <br> | |||
==Receiver Operation Characteristic (ROC)== <br> | |||
Wird genutzt um zu prüfen, ob das Modell gut ist. <br> | |||
→ Wie viele falsch positive, falsch negative, aber auch richtig positive und richtig negative Aussagen trifft das Modell? <br> | |||
{| class="wikitable float-left" style="text-align:center" | |||
| || ||colspan="3" style="text-align:center"| Mensch | |||
|- | |||
| || || '''Krebs''' || '''Gesund''' | |||
|- | |||
|rowspan="2"| Modellvorhersage | |||
| '''Krebs''' ||style="background:#B9FFC5 " | TP || style="background:#FFCBCB| FP | |||
|- | |||
| '''Gesund''' ||style="background:#FFCBCB| FN || style="background:#B9FFC5 " | TN | |||
|- | |||
|} | |||
Beispiel 'Krebs' = positiv, 'geund' = negativ | |||
* <span style="background:#B9FFC5"> TP</span>: True Positive (richtig positiv) → Modell sagt 'Krebs' richtig voraus. <br> | |||
*<span style="background:#B9FFC5"> TN</span>: True Negative (richtig negativ) → Modell sagt 'gesund' richtig voraus. <br> | |||
*<span style="background:#FFCBCB"> FP</span>: False Positive (falsch positiv) → Modell sagt der Patient hat Krebs, obwohl er gesund ist. <br> | |||
*<span style="background:#FFCBCB"> FN</span>: False Negative (falsch negativ) → Modell sagt 'gesund', obwohl der Patient Krebs hat. <br> | |||
Revision as of 00:46, 2 July 2019
Biomarker
Medizinische Biomarker
- Ein Biomarker ist ein messbarer Parameter biologischer Prozesse, der prognostische, oder diagnostische Aussagekraft hat und somit ein Indikator für Krankheiten, oder Umwelteinflüsse ist.
- Charakteristische biologische Merkmale, die objektiv gemessen werden können und auf einen normalen biologischen, oder krankhaften Prozess im Körper hinweisen können.
- Es können Zellen, Gene, Genprodukte, Enzyme, oder Hormone sein.
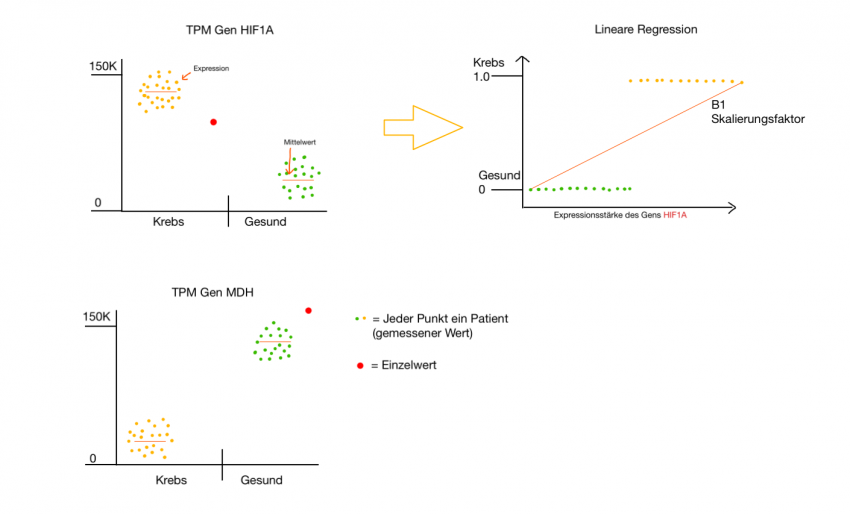 Wie in der Abbildung oben dargestellt, kann über Einzelwerte keine Aussage getroffen werden, ob der Patient krank oder gesund ist.
Wie in der Abbildung oben dargestellt, kann über Einzelwerte keine Aussage getroffen werden, ob der Patient krank oder gesund ist.
→ deswegen bedarf es mehrerer Biomarker
Frage:
Wie kann für einen TPM-Wert vorhergesagt werden, ob es sich um 'Krebs' oder 'gesund' handelt?
Logistische Funktion
[math]\displaystyle{ y = \beta_1 \cdot TPM_{HIF1\alpha} + \beta_0 }[/math]
[math]\displaystyle{ logit_{(P)} = log \frac{P}{1-P} }[/math]
- Damit wird die Wahrscheinlichkeit, dass jemand z.B. Krebs bekommt durch Gegenwahrscheinlichkeit bestimmt.
Biomarkersignatur
Erweiterung für mehrere Gene.
[math]\displaystyle{ P(x) = \frac{1}{e^{-((\beta)_1 \cdot x_1) + ((\beta)_2 \cdot x_1) + .... + (\beta)_n \cdot x_n) + \beta_0)}} }[/math]
Mashine learning
- Ein Modell muss zunächst von einem System erlent werden, dann kann das System eine Aussage treffen, ob z.B. 'krank' oder 'gesund'.
- Parameter [math]\displaystyle{ \beta_1 }[/math] und [math]\displaystyle{ \beta_0 }[/math] können nicht berechnet werden. → Müssen mit Hilfe eines Algorithmus geschätzt werden.
Maximum-Likelihood:
- Schätzung zur Parameterbestimmung.
- Training: Lerndaten sind bekannte Werte zur Aussage 'krank' oder 'gesund'
→ Algorithmus bestimmt einen genauen Wert für [math]\displaystyle{ \beta_1 }[/math], um krank (1) und gesund (0) zu bestimmen.
→ Danach kann mit dem Modell bestimmt werden, ob es gut oder schlecht ist.
- Problem: System versucht einen optimalen Wert zu finden
→ Overfitting: Zu genaue Beschreibung des Modells.
Frage: Wie gut ist die Qualität des Modells?
==Receiver Operation Characteristic (ROC)==
Wird genutzt um zu prüfen, ob das Modell gut ist.
→ Wie viele falsch positive, falsch negative, aber auch richtig positive und richtig negative Aussagen trifft das Modell?
| Mensch | ||||
| Krebs | Gesund | |||
| Modellvorhersage | Krebs | TP | FP | |
| Gesund | FN | TN | ||
Beispiel 'Krebs' = positiv, 'geund' = negativ
- TP: True Positive (richtig positiv) → Modell sagt 'Krebs' richtig voraus.
- TN: True Negative (richtig negativ) → Modell sagt 'gesund' richtig voraus.
- FP: False Positive (falsch positiv) → Modell sagt der Patient hat Krebs, obwohl er gesund ist.
- FN: False Negative (falsch negativ) → Modell sagt 'gesund', obwohl der Patient Krebs hat.